怎么做网站镜像境外公司注册
环境:centos 7 ,64位
1、创建一个指定的文件夹作为安装示例所用,该示例文件夹为“hsk-nwct”。“hsk-nwct”内创建“app”文件夹作为docker容器挂载出来的文件。
2、在“app”内下载花生壳linux安装包,下载花生壳应用:花生壳客户端官方下载 - 贝锐花生壳官网
本服务下载的版本是“phddns_5.2.0_amd64.rpm”,然后创建容器内执行的安装命令文件“a.sh”。“a.sh”文件内容
#!/bin/sh
a="开始启动 docker phddns 花生壳服务"
echo $aecho "进入安装包所在文件夹"
cd app/echo "花生壳服务检测"if command -v phddns >/dev/null 2>&1;then echo "服务已安装"phddns statuselse echo "服务未安装,执行安装"rpm -ivh phddns_5.2.0_amd64.rpmecho "服务完成、设置开机启动"phddns enablefi该命令是先检测容器内有没有安装过花生壳应用,没有则执行安装的流程。
3、退出“app”文件,在“hsk-nwct”内运行容器。执行如下命令:
docker run --privileged=true --restart=always -e TZ="Asia/Shanghai" \
-d --net=host --name hskct2023 \
-v /root/docker/hsk-nwct/app:/app \
dokken/centos-7:latest 第一次运行,可以考虑将“ --restart=always”去掉,方便查看容器是否运行成功,使用如下命令:
docker logs hskct20234、在运行的容器内安装花生壳,命令如下:
docker exec -it hskct2023 /bin/bash /app/a.sh执行完后,可以看到如下
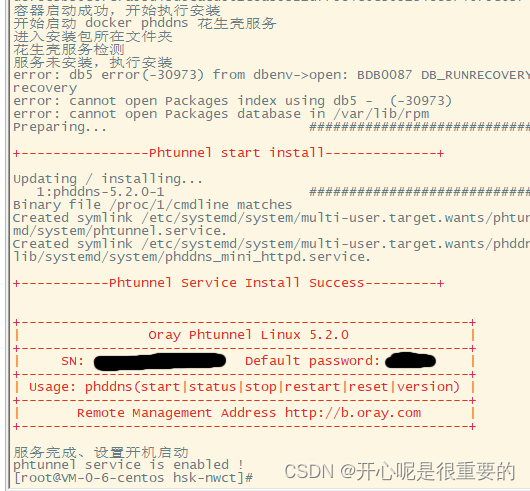
可以考虑在容器内继续执行 ”phddns status“ 查看是否启动成功。记住 ”sn“码,将它绑定到“设备列表”即可,管理端地址是:花生壳管理 。
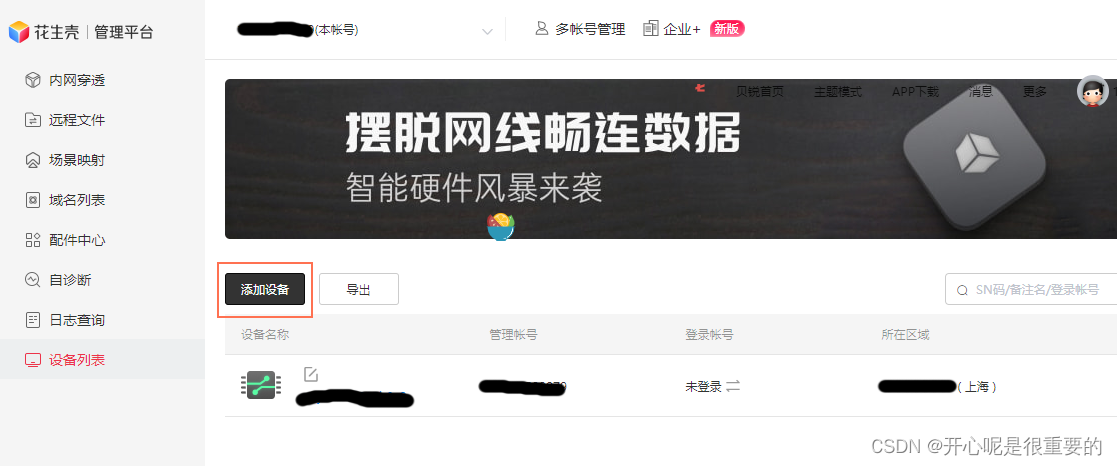
如图配置好了。
5、试错展示,最开始时是将第3、第4 步的两个命令合在一起的,后来发现,容器运行一会儿就自动退出了,查看日志也是提示安装成功了,并没有其他什么报错。后来了解到容器运行就退出的几个原因:
- docker容器运行必须有一个前台进程, 如果没有前台进程执行,容器认为空闲,就会自行退出
- 容器运行的命令如果不是那些一直挂起的命令( 运行top,tail、循环等),就是会自动退出
- 这个是 docker 的机制问题
很明显, 第四步的执行“a.sh”的命令并不会一直挂着的,所以他会安装完花生壳应用就自己关闭退出了。试错命令如下:
docker run --privileged=true --restart=always -e TZ="Asia/Shanghai" \
-d --net=host --name hskct2023 \
-v /root/docker/hsk-nwct/app:/app \
dokken/centos-7:latest /bin/bash /app/a.sh6、每次都要输入命令,为图方便,我将需要执行的命令整合了一下。在“hsk-nwct”内创建“test.sh”文件,内编辑
#!/bin/sh
a="开始启动 docker hsk 花生壳内外网穿透 服务"
echo $adocker stop hskct2023
docker rm hskct2023docker run --privileged=true --restart=always -e TZ="Asia/Shanghai" \
-d --net=host --name hskct2023 \
-v /root/docker/hsk-nwct/app:/app \
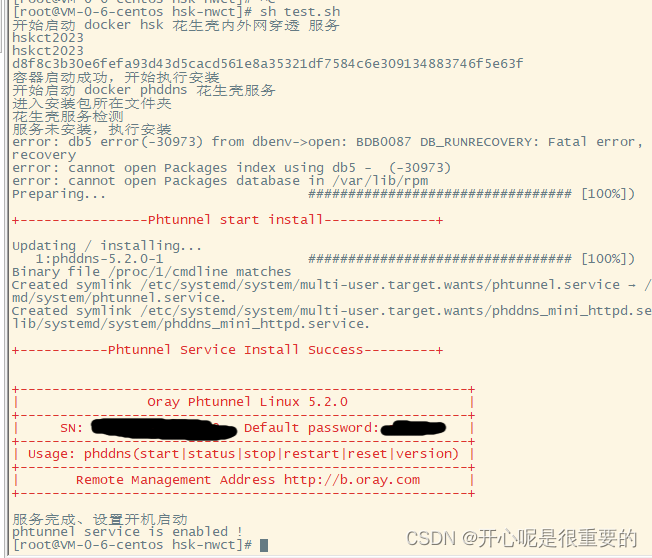
dokken/centos-7:latest echo "容器启动成功,开始执行安装"docker exec -it hskct2023 /bin/bash /app/a.shexit
exit运行成功的示例:
7、其他命令,记录一下方便回顾:
删除花生壳的命令:yum remove phddns -y
